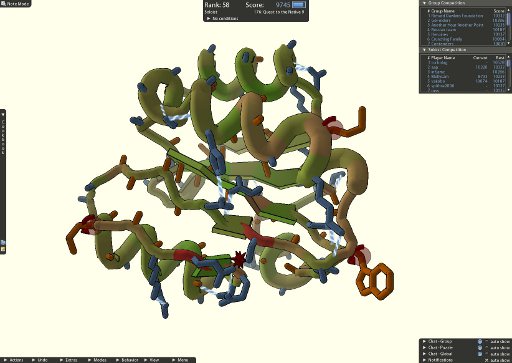
Forscher scheiterten bislang ? Laien gelang jetzt der Durchbruch: Computerspieler haben mit Hilfe einer frei im Internet verfügbaren Software die dreidimensionale Struktur eines Proteins enträtselt, das Wissenschaftlern zuvor Kopfzerbrechen bereitete. Es handelt sich um ein Enzym, das bei der Vermehrung des HI-Virus im Körper eine große Rolle spielt. Um Medikamente entwickeln zu können, die das Enzym beeinflussen, muss der molekulare Aufbau dieses Eiweißkörperchens bekannt sein. Die von den Spielern gelieferten Entwürfe machen es nun möglich, an der Entwicklung von AIDS-Medikamenten zu arbeiten, schreiben die Wissenschaftler um David Baker von der University of Washington in einem Artikel im Journal „Nature Structural & Molecular Biology“. Die Spieler sind als Co-Autoren der Studie namentlich aufgeführt. Das spektakuläre Ergebnis zeige eindrucksvoll das Potenzial, das in spielerischer Annäherung an wissenschaftliche Fragestellungen stecke, so die Forscher.
Im Kampf gegen das HI-Virus gelten Medikamente, die sich gezielt an bestimmte Bestandteile des Erregers koppeln, als besonders vielversprechend. Die Entwicklung solcher passgenauen Wirkstoffe ist allerdings schwierig, denn Proteine bestehen aus einer Vielzahl von kleinen Bausteinen, den Aminosäuren, die kompliziert zusammengesetzt sind. Selbst für ein vergleichsweise kleines Protein müssen Wissenschaftler deshalb aufwendige Berechnungen durchführen und oft misslingt die Computer-gestütze Strukturanalyse ganz. „Wir wollten deshalb herausfinden, ob menschliche Intuition erfolgreich sein kann, wo automatisierte Methoden bislang versagt haben“, sagt David Baker.
Die Computerspieler nutzten ein Spiel namens „Foldit“, mit dem Laien genauso wie Biochemiker an der dreidimensionalen Struktur von Molekülen basteln können. Mit dieser Software lassen sich die einzelnen Bestandteile von Proteinen frei drehen und zusammensetzten, bis wie beim Drehen an einem Zauberwürfel alles passt. Die Forscher um Baker versuchten gezielt, möglichst viele Mitspieler einzubeziehen – mehr als hundert Einzelpersonen und Spielergruppen waren letztendlich beteiligt. Die Wissenschaftler stellten den Spielern alle bekannten Informationen zum Aufbau des Enzyms zur Verfügung. Es gelang, den Ehrgeiz der Teilnehmer zu wecken: Sie bildeten Spielergruppen mit Namen wie „Foldit Void Crushers Group“ oder „Foldit Contender Group“, die sich im Entwurf eines schlüssigen Modells der Enzymstrukur maßen.
Innerhalb von drei Wochen gelang es den Spielern auf diese Weise, ein realistisches Modell des komplexen Proteinkörpers zu entwickeln. „Computerspiele eröffnen die Möglichkeit, die dreidimensionale Vorstellungskraft des Menschen mit der Leistung eines Computers zu kombinieren“, sagen die Wissenschaftler. Sie wollen nun die Einsatzmöglichkeiten dieses Konzepts auch für die Lösung weiterer wissenschaftlicher Fragestellungen ausloten.
Firas Khatib, University of Washington, et al.: Nature Structural & Molecular Biology, doi:10.1038/nsmb.2119 wissenschaft.de –
Martin Vieweg